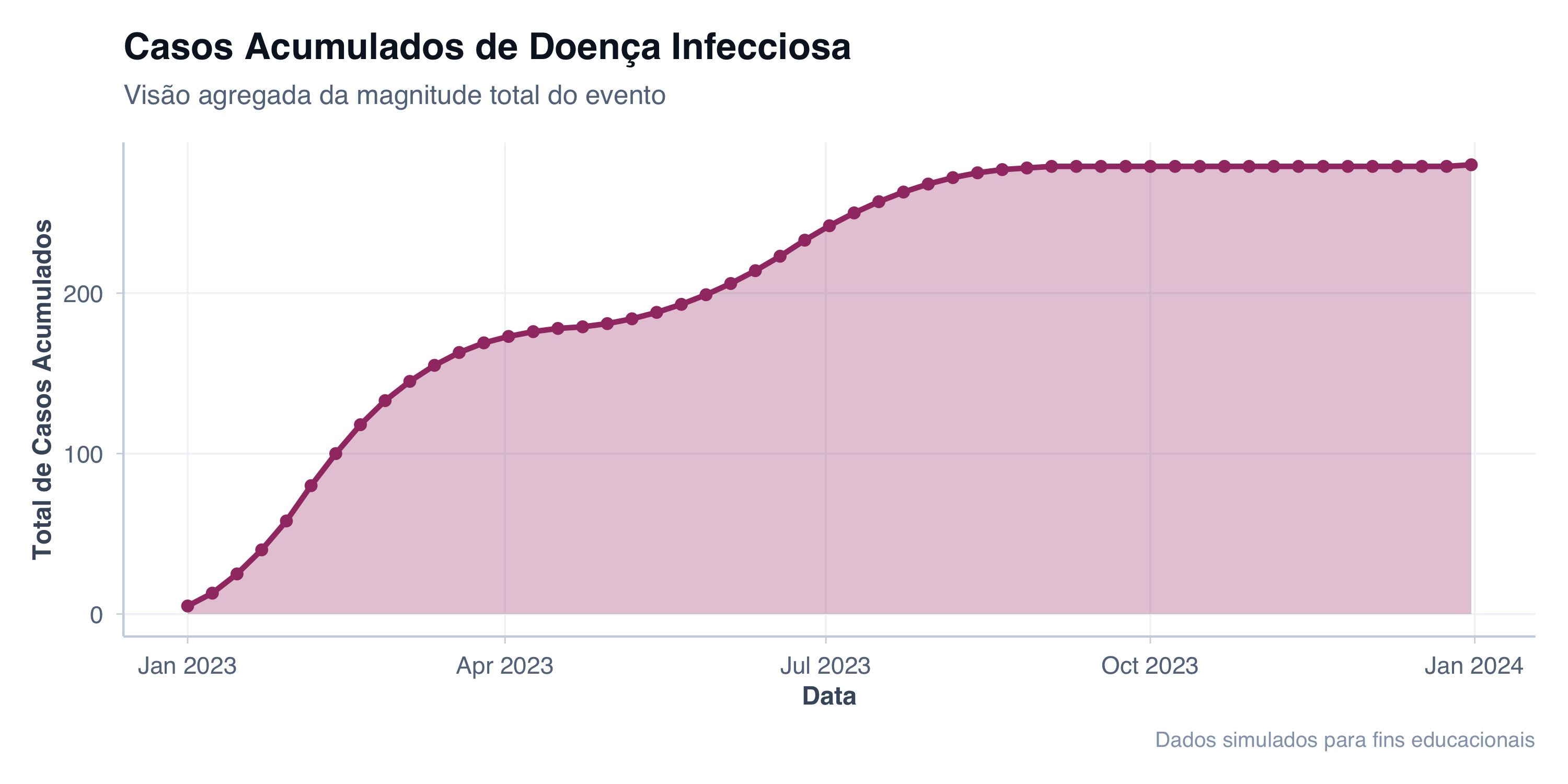
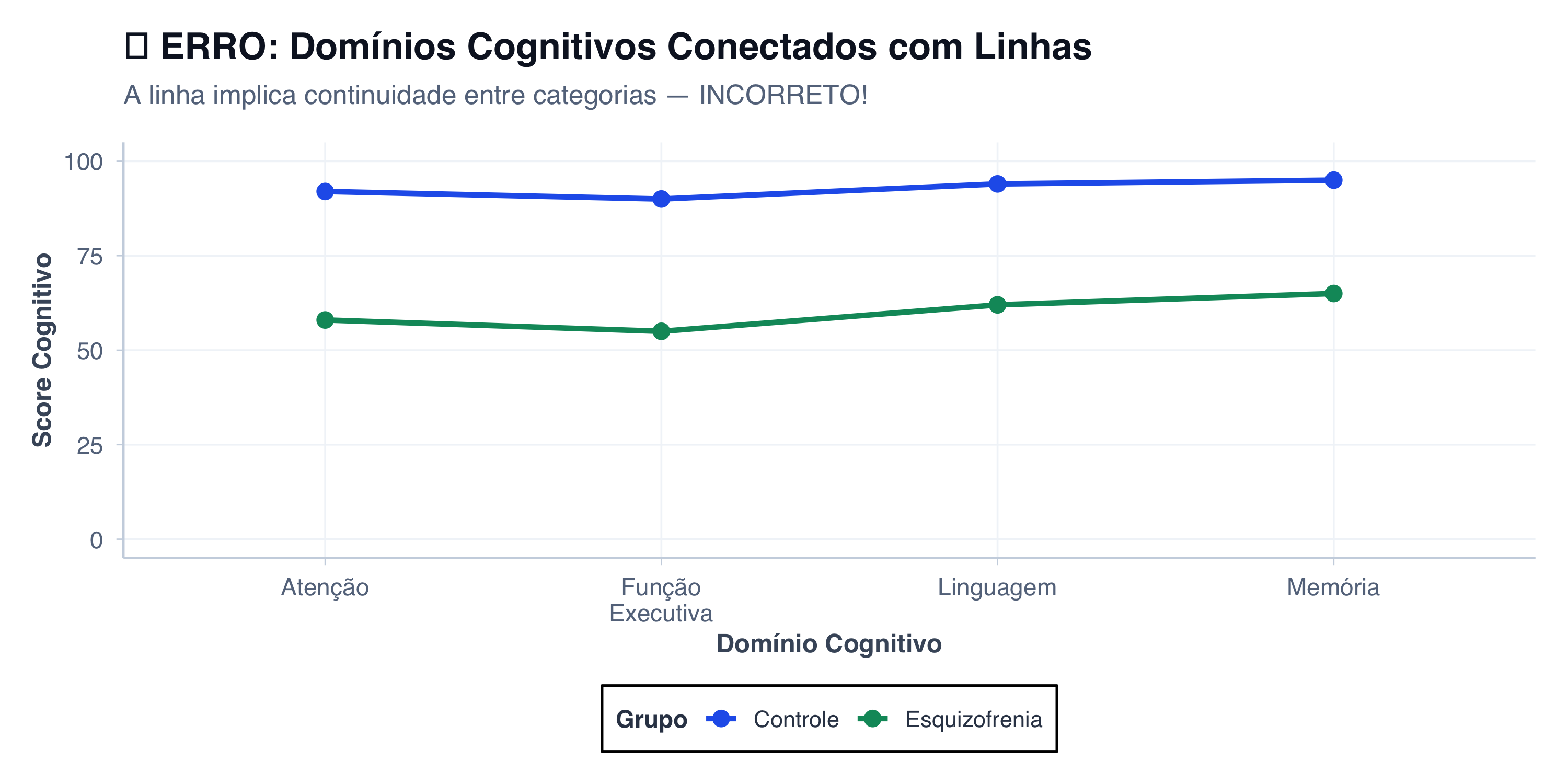
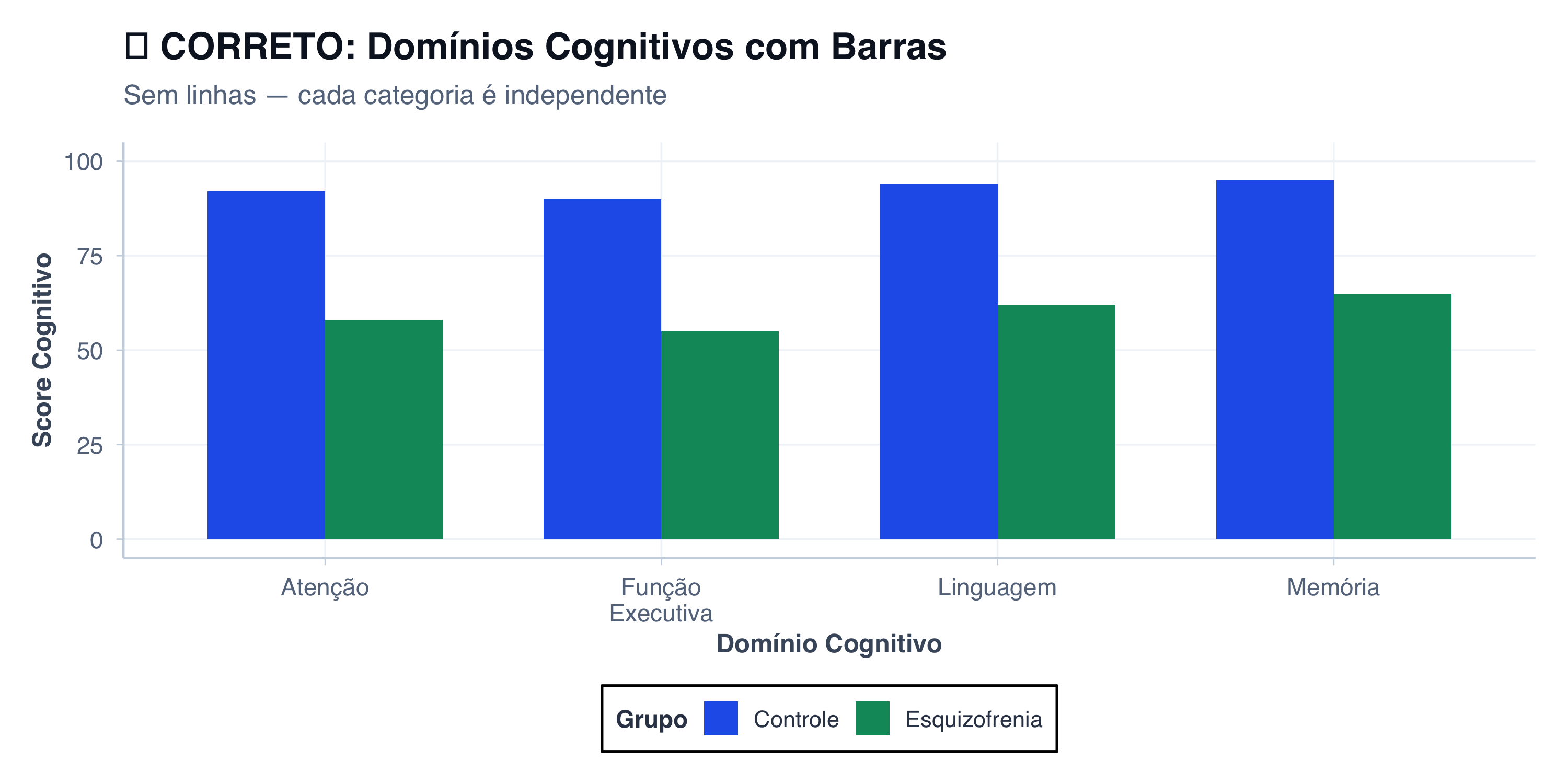
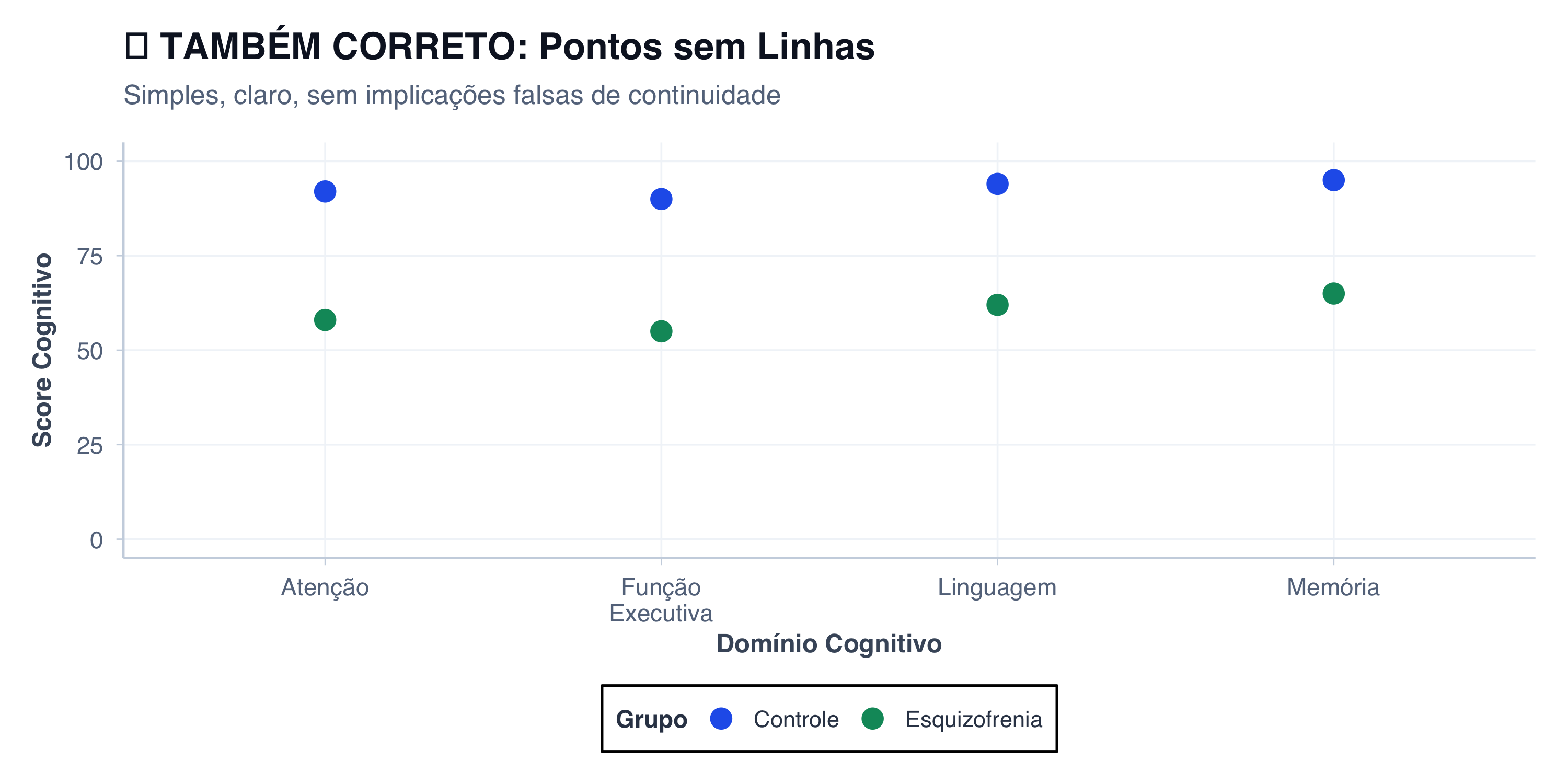
# Dados de casos confirmados acumulados
dados_casos <- tibble(
data = seq(as.Date("2023-01-01"), as.Date("2023-12-31"), by = "week"),
casos_novos = c(5, 8, 12, 15, 18, 22, 20, 18, 15, 12, 10, 8, 6, 4, 3, 2, 1,
2, 3, 4, 5, 6, 7, 8, 9, 10, 9, 8, 7, 6, 5, 4, 3, 2, 1, 1,
0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1)
) %>%
mutate(casos_acumulados = cumsum(casos_novos))
ggplot(dados_casos, aes(x = data, y = casos_acumulados)) +
geom_area(fill = "#A23B72", alpha = 0.3) +
geom_line(color = "#A23B72", linewidth = 1.2) +
geom_point(color = "#A23B72", size = 2) +
tema_graficos() +
labs(
title = "Casos Acumulados de Doença Infecciosa",
subtitle = "Visão agregada da magnitude total do evento",
x = "Data",
y = "Total de Casos Acumulados",
caption = "Dados simulados para fins educacionais"
) +
scale_y_continuous(limits = c(0, NA))